circRNA很红,这个大家都知道。尤其是它身上那份高大上的神秘感,引得一众科学家瞬间产生扑倒circRNA的好奇感,并期望能看到该领域中更多不一样的风景。
但眼下circRNA研究的一个巨大挑战就是,有关circRNA的可参考信息不多,怎么往下研究也没有目标。为了让大家早日玩转circRNA,则本文推荐六款非常Powerful的在线分析神器来助大家一臂之力。
circRNA基本信息分析神器:circBase
目前,数据库circBase(http://www.circbase.org/)收集包括以下6个物种的circRNA信息:人 (hg19)、小鼠(mm9) 、秀丽线虫(ce6)、黑腹果蝇 (dm3)、矛尾鱼 (latCha1)、腔棘鱼 (latCha1)。
该数据库最新版本发布时间为2017年6月,可帮助大家对筛选验证的circRNA有个具体的认识,还可直接下载到相关序列信息和注释信息,其界面打开如下。
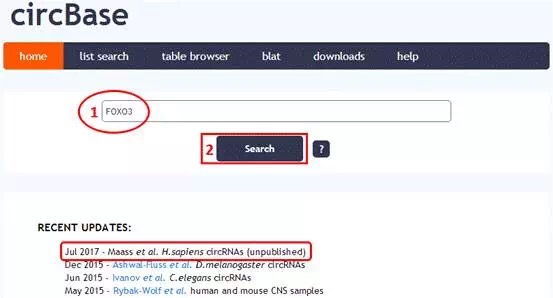
在主页中间搜索框中输入基因名称,这里以“FOXO3”基因为例进行操作演示,点击“search”按钮。
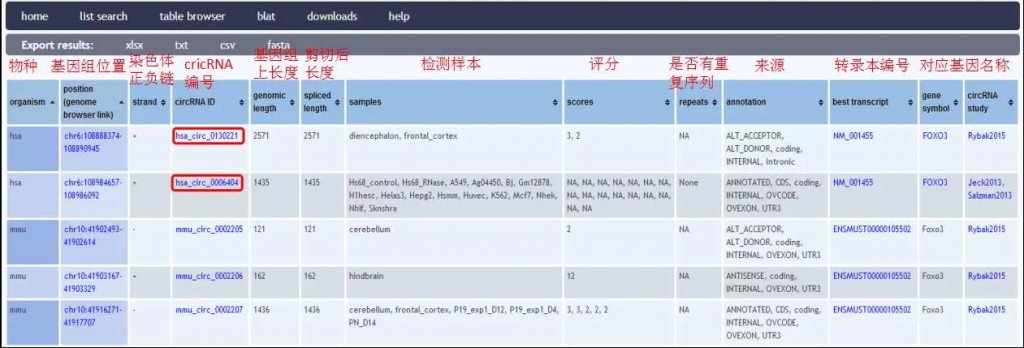
对照搜索结果,对circRNA信息进行核对,下图可以看出人的FOXO3基因组序列上对应两个circRNA,分别是hsa_circ_0130221和hsa_circ_0006404。
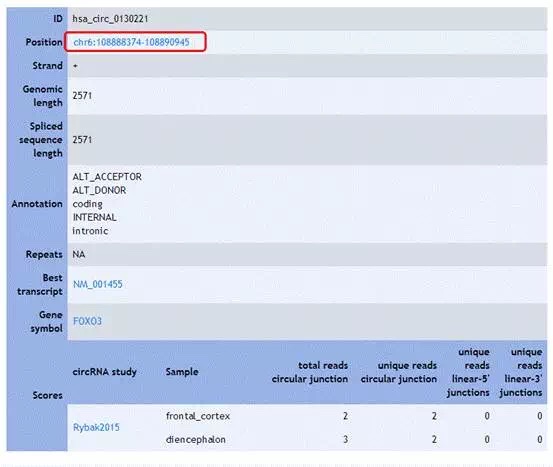
上述搜索结果表格中的蓝色字体标记的文字都包含超链接,可以进一步点开查看详细信息。在点击hsa_circ_0130221后,可跳转其详细信息界面。
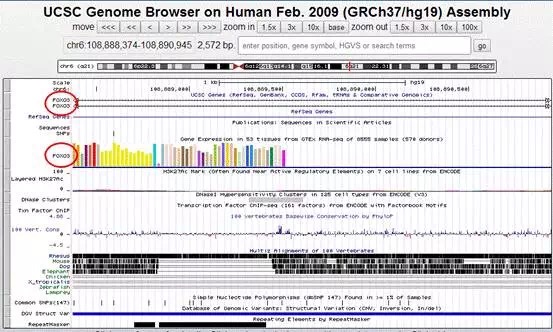
点击hsa_circ_0130221下行的Position,则跳转UCSC基因组浏览器界面。下图即可形象地展示FOXO3相关circRNA hsa_circ_0130221的基因组信息了。
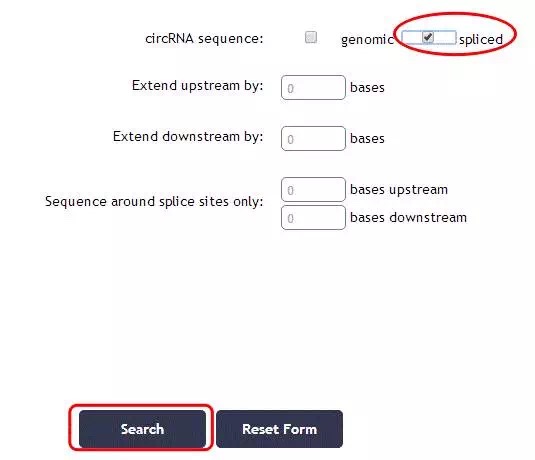
输出circRNA的序列时,可在搜索界面中点击export results中的Fasta,可跳转以下界面:
在circRNA sequence中选择“spliced”,下方选“search”后即可得到成环序列;选择“genomic”,下方选择“Extend upstream by 1000 bases”即可得到上游延伸1000bp的包含成环以及内含子的序列。
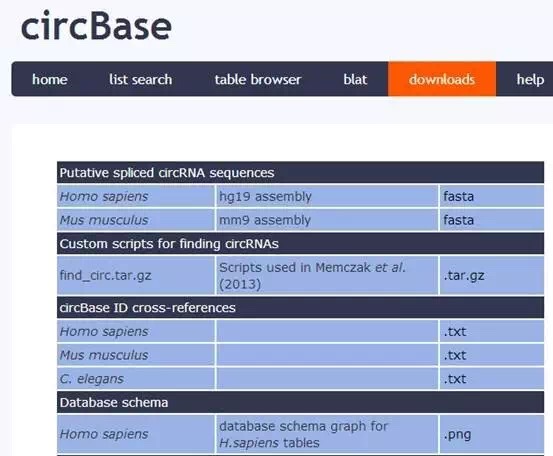
可能有些做组学研究的小伙伴们需要整个物种的circRNAs序列信息,在这种情况下,大家只需要在工具栏“downloads”项进行选择,找到对应的物种,点击下载就可以了:
ceRNA功能研究数据库:circNet
CircNet(http://circnet.mbc.nctu.edu.tw/)利用464个RNA-seq测序数据,进行新circRNA预测及基因组注释,并计算已知的及新预测的circRNA表达情况,构建circRNA-miRNA-gene调控网络,以上信息均可从该数据库获得。
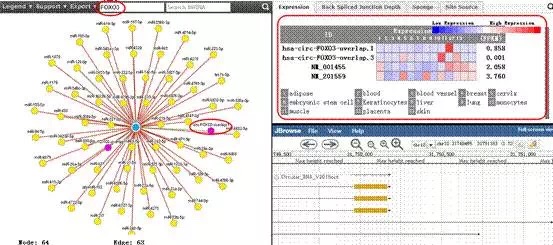
以FOXO3为例,在打开的界面中,直接在搜索框中输入FOXO3,其结果如下:
如图所示,不仅显示了FOXO3相关的环状RNA circ-FOXO3.1,还显示了microRNA,右侧上面点击Expression则会显示circ-FOXO3.1在不同组织中的表达水平,右侧下面可以根据位置对 circ-FOXO3.1进行查询显示。
circRNA人疾病相关联数据库:circ2Traits
Circ2Traits(http://gyanxet-beta.com/circdb/)是一个收集与人类疾病或性状潜在关联的circRNA数据库,可通过预测miRNAs和人类的蛋白质编码基因、长链非编码基因及环状RNA间的相互作用关系,构建了相互作用网络,并对miRNAs-circRNA相互作用组中的蛋白编码基因进行了GO富集分析;此外,将与疾病相关的SNPs位点定位到circRNA基因座上,并鉴定了环状RNAs上的Ago相互作用位点。
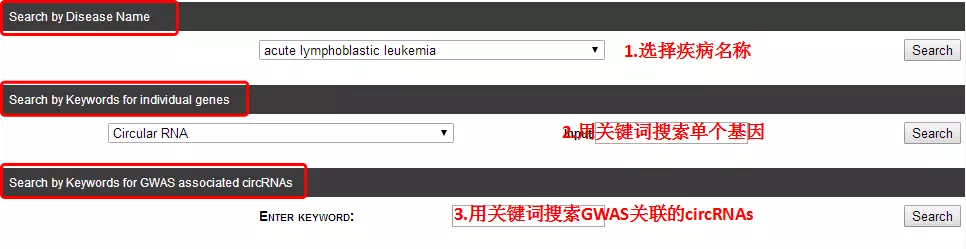
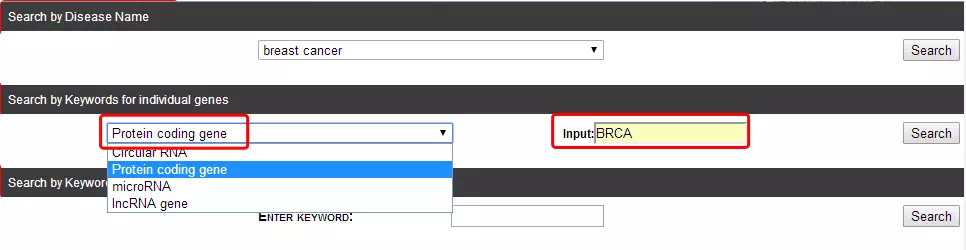
其界面打开后可看到三个功能模块,如下图所示。在下拉框中选择相应疾病名称后,点击Search即可查看与该疾病相关的circRNA。
以BRCA基因为例,在Search by keywords for individual genes中左下拉框中选择Protein coding gene,并在Input后输入BRCA基因后,点击search按钮。
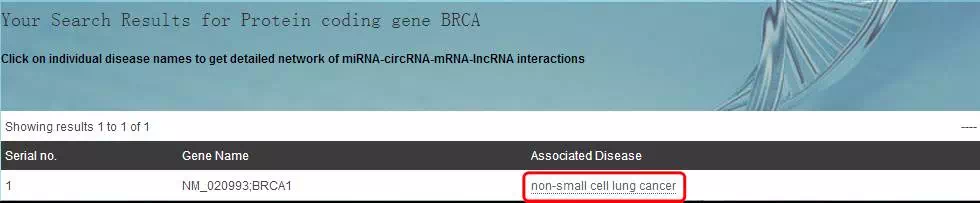
其结果如下,点击Associated Disease中的non-small cell lung cancer后,可跳转至新的界面。
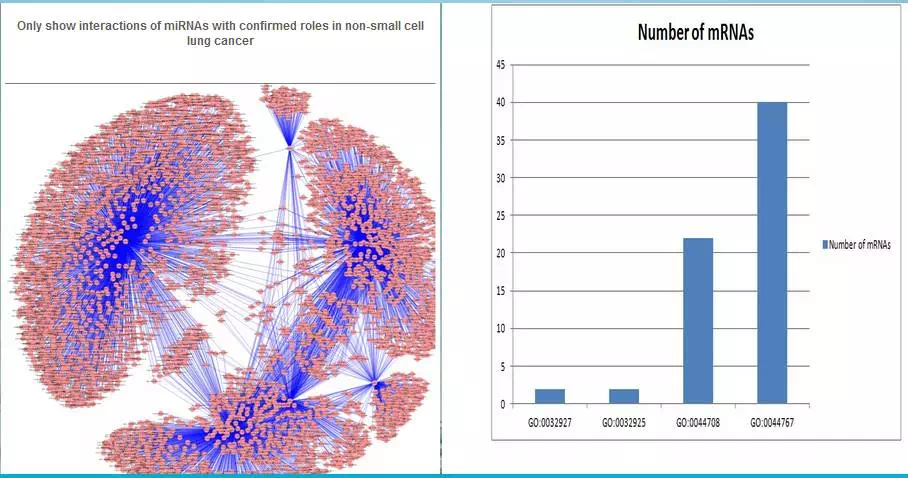
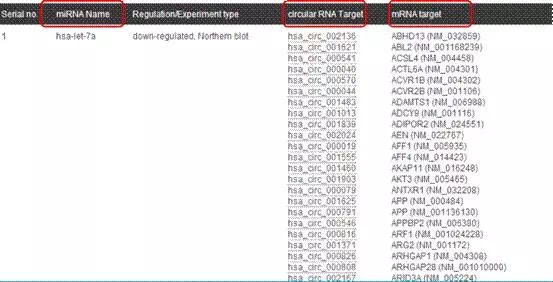
点击左图中任一个橙色点,则会出现以下结果:
circRNA组织特异性分布数据库:TSCD
TSCD数据库 (http://gb.whu.edu.cn/TSCD/)是检索人和小鼠中组织特异性的circRNA信息的数据库,也包括成人和胚胎的不同组织。对于想了解不同组织中的特异性表达的circRNA,可以在该数据库进行检索。
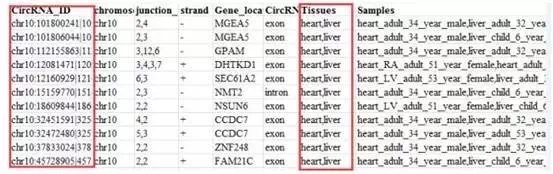
以查询“人的胎儿中心脏和肝脏组织共有的circRNA”为例,首先进入网站后点击 Comparsion,选择“Heart”和“liver”
submit提交得到一份结果文本,文本中收录的便是心脏和肝脏组织共有的circRNA信息。
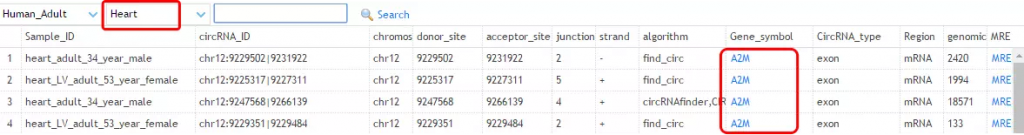
以查询“人的心脏组织中以A2M为线性母本基因形成的circRNA”为例。进入网站TSCD后点击 Browser-hg19/mm9 , 选择 Human-Adult和Heart,并在搜索框内键入“A2M”,得到如下结果:
点击“A2M”,可以查看A2M作为线性母本形成circRNA的情况,并以图片和表格两种形式呈现。
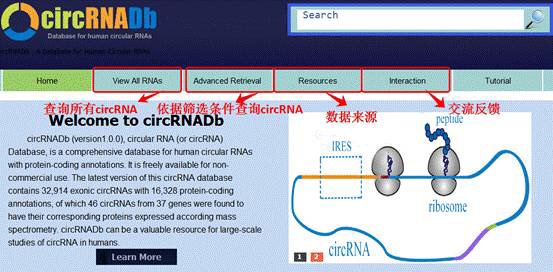
circRNA编码蛋白数据库:circRNADb
circRNAdb数据库 (http://202.195.183.4:8000/circrnadb/circRNADb.php)共收录了32914条人类外显子circRNA记录,每条记录都包括基因组位置信息,RNA编辑情况,所对应的基因组序列,IRES序列元件,预测的ORF(Open Reading Frame)以及相关的参考文献。
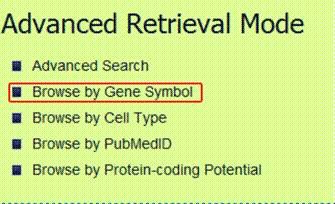
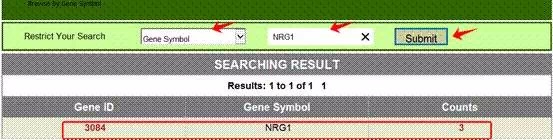
该网站主界面清晰,设计人性化,在Advance Retrieval可以根据基因名称(Gene symbol),PubMed ID及细胞或组织类型等多种检索条件,满足不同查询需求。查询以NRG1基因为线性基因的circRNA为例。
点击Advance Retrieval——Browse by Gene Symbol,选择Gene Symbol后,在搜索框中输入“NRG1”,提交后可发现NRG1这个基因可形成3种circRNA。
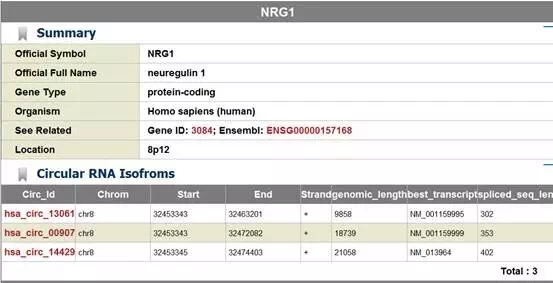
点击进入新的界面,这三个circRNA分别是hsa_circ_13061、hsa_circ_00907和hsa_circ_14429,具体情况可点击名称进一步查看。
预测结合靶点的数据库:CircInteractome
数据库CircInteractome (https://circinteractome.nia.nih.gov/)预测了已知的109个RNA结合蛋白数据集与circbase中的circRNA的结合位点,并利用Targetscan软件预测了miRNAs与circRNA的潜在结合位点。可进行circRNA分子检索、circRNA结合蛋白预测、PCR引物设计、siRNA干扰序列设计等操作。
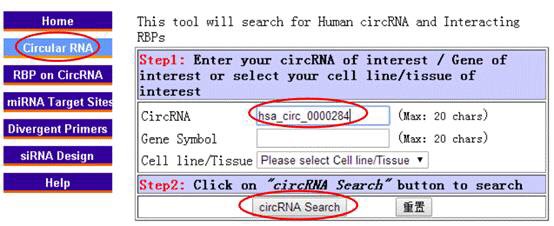
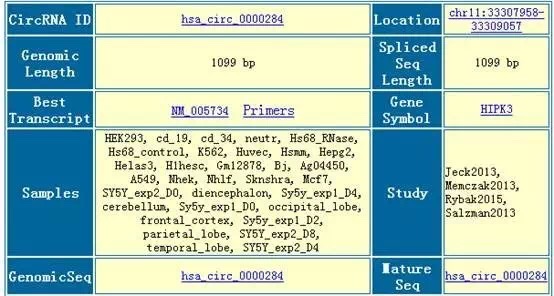
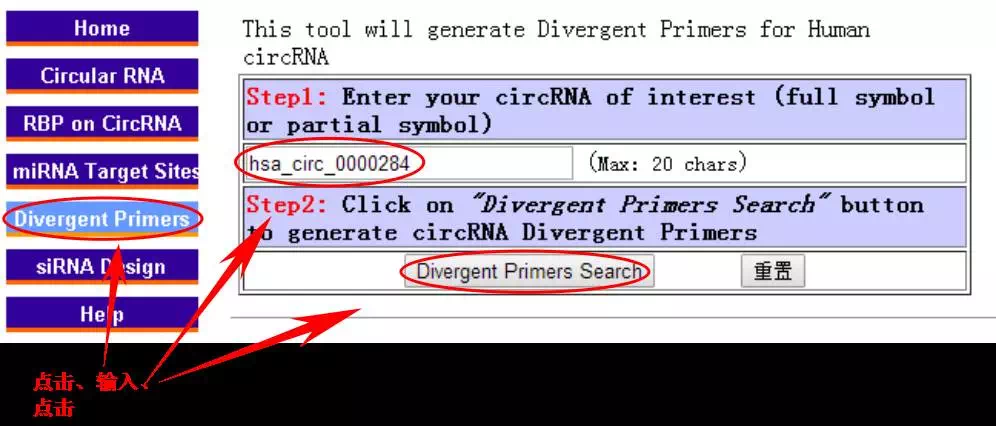
1、circRNA分子检索:以hsa_circ_0000284为例,在circular RNA的界面中输入hsa_circ_0000284后,点击cirRNA search即可获取circRNA详细信息。
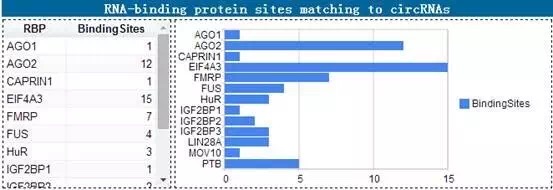
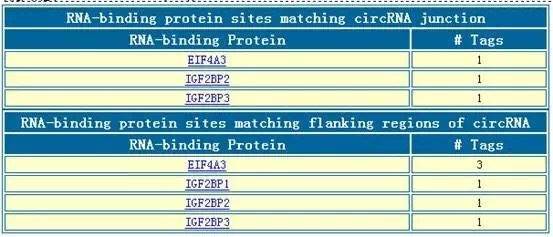
此外,还会显示circRNA的上RBP结合位点,分析circRNA作为RBP蛋白‘sponge’或‘decoy’的可能性;以及circRNA的junction和Flanking序列可能结合的RBP蛋白信息,其结果如下图所示:
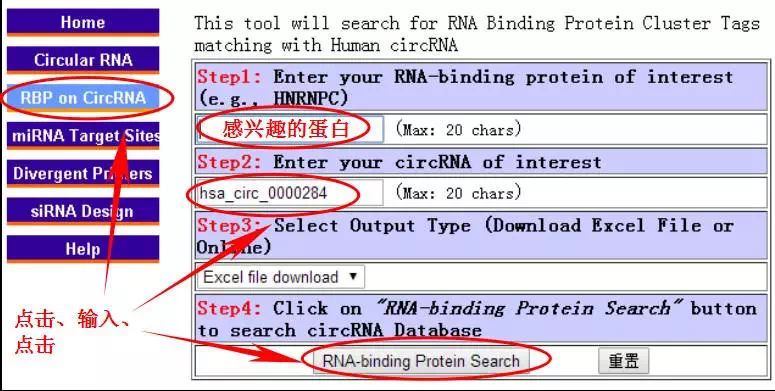
而当你想知道某个RBP是否能结合感兴趣的circRNAs时,只要在该网站RBP on CircRNA这个界面中进行检索预测即可。
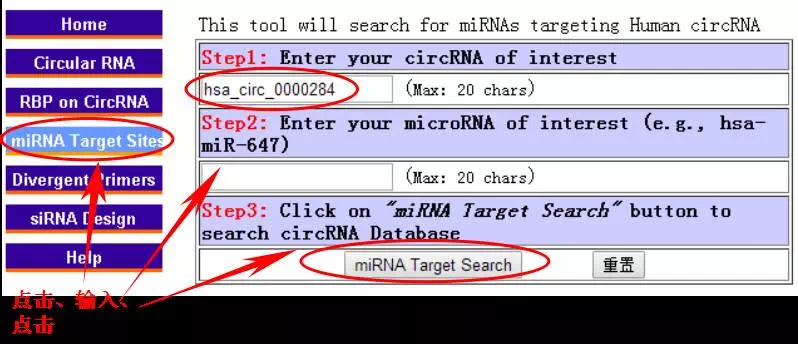
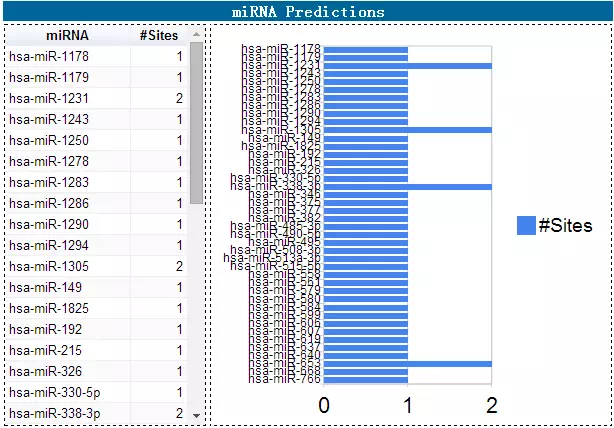
2、circRNA结合miRNA预测:目前最常见的circRNA功能研究就是其以ceRNA机制发挥生物学功能。因而只要输入感兴趣的circRNA和感兴趣的miRNA,就可以预测到他们可能的结合位点信息。如果结果显示有,您只要根据该信息就行后期验证就可以了。
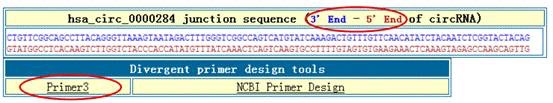
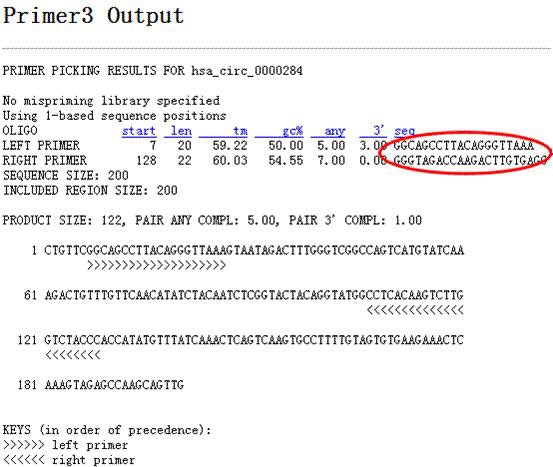
3、circRNA验证反向引物设计:输入circRNA分子后,点击Divergent primers search,即可获得所查询circRNA分子的junction sequence,下面还附带了2个PCR引物设计工具primer3和NCBI primer design,研究者可自行选择。
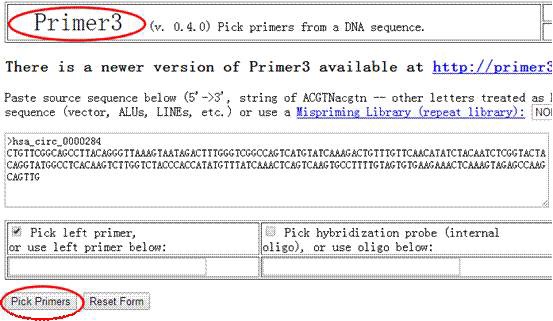
点击Primer3,页面跳转到Primer3网站,点击“Pick Primers”按钮。即可获得特异性引物序列。
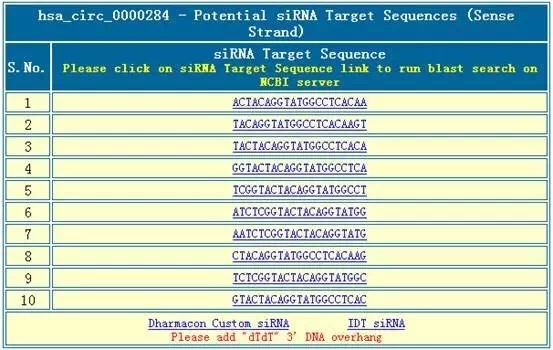
4、circRNA siRNA设计:CircInteractome将会提供10个候选siRNA片段;随后可根据siRNA评分标准选择合适的siRNA片段。评分标准包括G/C含量30-60%,最后一个碱基为A/U等。
circRNA翻译潜能预测网站
circRNA是否具有翻译潜能,首先得看其是否拥有开放阅读框(ORF),其次得看其是否具有内在的核糖体进入结合位点(Internal Ribosome Entry Site,IRES)。为此,这两款在线软件大家就一定要记住了。
1、 ORF Finder (https://www.ncbi.nlm.nih.gov/orffinder/),只要输入circRNA的序列信息,就可以直接看到ORF区域了。
2、IRESite (http://iresite.org/IRESite_web.php),基于已有68个病毒和115个真核细胞的实验数据,收录了大量的具有IRES位点的基因。因此,将感兴趣的circRNA的序列输入比对,就能预测circRNA是否具有IRES位点。









您好,怎么看某一个circRNA的成环类型呢?annot_exon?
circNet登陆不了
棒,很有用